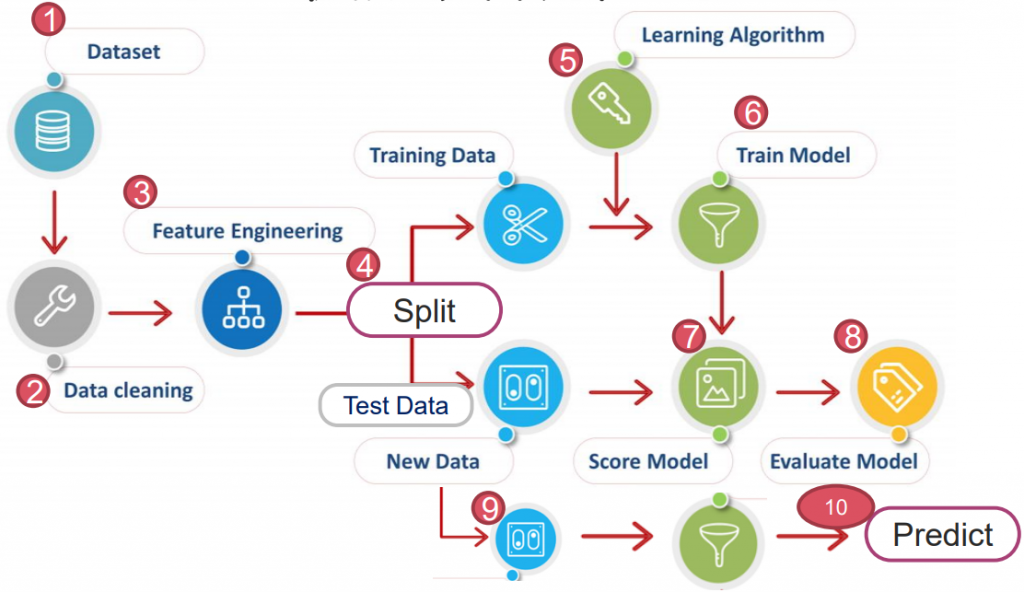
https://yourfreetemplates.com/free-machine-learning-diagram/
本篇會著重在先前提過的非監督式學習上。
它是機器學習的一種方法,在沒有標記的訓練集中,讓學習器對輸入的資料進行分類。
非監督學習主要藉由:聚類分析(cluster analysis)、關聯規則(association rule)、維度縮減(dimensionality reduce)達成最終的分群。
而本篇會著重在 Cluster analysis 聚類分析上。
把相似的物件通過靜態分類成不同的組別或者更多的 subset,讓同子集中的物件都有相似屬性。
依照分類方式,又分為:
Hard Clustering:數據集中的樣本都被「100%」分到某一類別中。
Soft Clustering:數據集中的樣本以「一定的概率」被分到某一類別中。
即是一種硬聚類。透過不停迭代求解,直至分類到指定聚類數量,又稱 EM 分析。
Expectation-step: 求得每個聚類的重心(mean)
Maximization-step: 把資料點歸屬給距離最近的聚類重心。
詳細步驟為:
打個比方:假設有一資料集 (5,20,11,5,3,19,30,3,15)
至此,所有資料點不再更動,即完成。
但 k-means 的缺點如下:
K-means++ 改善了初始重心選取不當的問題。核心思想:初始的聚類重心間距要盡可能遠。
步驟如下:
以 make_blobs 創建的隨機亂數為例:
from sklearn.datasets import make_blobs
X, y_true = make_blobs(
n_samples=300,
centers=4,
cluster_std=0.6,
random_state=0
)
from sklearn.cluster import KMeans
km = KMeans(
n_clusters=4,
random_state=0
)
km.fit(X)
y_pred = km.predict(X)
參數:
1. n_clusters: 即 k 值。默認 8。
2. max_iter: 執行一次 k-means 算法所進行的最大迭代數。默認 300。
3. n_init: k-means 算法會隨機運行 n 次,將最好的聚類作初始化的結果。默認 10。
4. verbose: 列出優化過程。默認 0。
5. init: 初始化方法,有 ‘k-means++’(默認), ‘random’ 或 nd-array。
更多的超參數可參考:https://www.twblogs.net/a/5b8aaade2b71775d1ce86b48
y_true[:20], y_pred[:20]
>> (array([1, 3, 0, 3, 1, 1, 2, 0, 3, 3, 2, 3, 0, 3, 1, 0, 0, 1, 2, 2]),
array([0, 2, 1, 2, 0, 0, 3, 1, 2, 2, 3, 2, 1, 2, 0, 1, 1, 0, 3, 3]))
若我們把不同類別的 index 列舉出來比較,會發現其實它們被分配到同個群:
import pandas as pd
true = pd.Series(y_true)
pred = pd.Series(y_pred)
print(true[true==1].index)
print(pred[pred==0].index)

# 在圖上標示重心
plt.scatter(X[:, 0], X[:, 1], c=y_pred, s=50, cmap='viridis')
centers = km.cluster_centers_
plt.scatter(centers[:, 0], centers[:, 1], c='red', s=200, alpha=0.5)
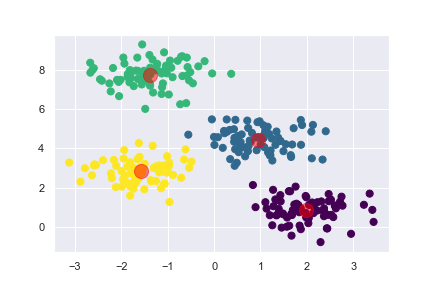
解決了初始聚類重心的難題後,接著我們來解決 k 值選定。
使用 make_blobs 產生的資料作以下兩種範例:
# 圖片美化用
import seaborn as sns; sns.set()
from sklearn.datasets import make_blobs
X, y_true = make_blobs(
n_samples=150,
n_features=2,
centers=3,
cluster_std=0.5,
shuffle=True,
random_state=0
)
plt.scatter(X[:, 0], X[:, 1], c=y_true, s=50)
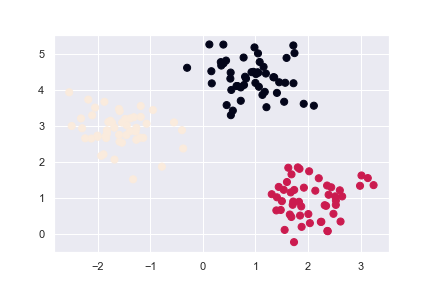
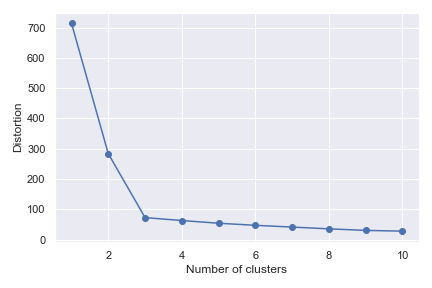
以迭代集群數去執行 k-means,用誤差平方和(MSE)作為失真(Distortion)準度。
from sklearn.cluster import KMeans
distortions = []
# 用迭代將 1~10 都試一次
for i in range(1, 11):
km = KMeans(
n_clusters=i,
n_init=10,
max_iter=300,
random_state=0
)
km.fit(X)
# 樣本到它們最近的聚類中心的距離平方和(越小越好)
distortions.append(km.inertia_)
# 作圖
import matplotlib.pyplot as plt
plt.plot(range(1, 11), distortions, marker='o')
plt.xlabel('Number of clusters')
plt.ylabel('Distortion')
plt.tight_layout()
plt.show()
首先定義 Silhouette 輪廓如下: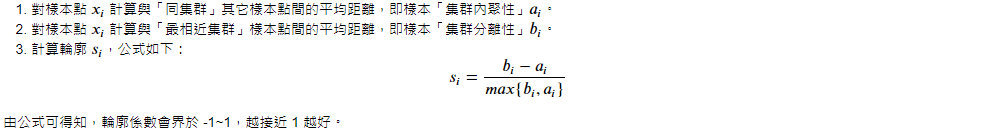
使用 sklearn 內建計算輪廓係數:
for i in range(2, 11):
km = KMeans(
n_clusters=i,
n_init=10,
max_iter=300,
random_state=0
)
km.fit(X)
y_pred = km.fit_predict(X)
print(f'{i:<2}, silhouette score: {silhouette_score(X, y_pred):.2f}')
>> 2 , silhouette score: 0.58
3 , silhouette score: 0.71
4 , silhouette score: 0.58
5 , silhouette score: 0.45
6 , silhouette score: 0.32
7 , silhouette score: 0.32
8 , silhouette score: 0.34
9 , silhouette score: 0.35
10, silhouette score: 0.35
可以發現當分群 3 時,輪廓係數最高。我們可以把它視覺化:
# k=3
from sklearn.cluster import KMeans
km = KMeans(n_clusters=3, n_init=10, max_iter=300, random_state=0)
y_pred = km.fit_predict(X)
import numpy as np
cluster_labels = np.unique(y_pred)
n_clusters = cluster_labels.shape[0]
from sklearn.metrics import silhouette_samples
sil = silhouette_samples(X, y_pred, metric='euclidean')
from matplotlib import cm
y_low, y_upp = 0, 0
yticks = []
# i: 1~3, c: 0~2
for i, c in enumerate(cluster_labels):
c_sil = sil[y_pred == c]
c_sil.sort()
y_upp += len(c_sil)
color = cm.jet(float(i) / n_clusters)
plt.barh(
range(y_low, y_upp),
c_sil,
height=1.0,
edgecolor='none',
color=color
)
yticks.append((y_low + y_upp) / 2.)
y_low += len(c_sil)
sil_avg = np.mean(sil)
plt.axvline(sil_avg, color="r", linestyle="--")
plt.yticks(yticks, cluster_labels + 1)
plt.ylabel('Cluster')
plt.xlabel('Silhouette coefficient')
plt.tight_layout()
plt.show()
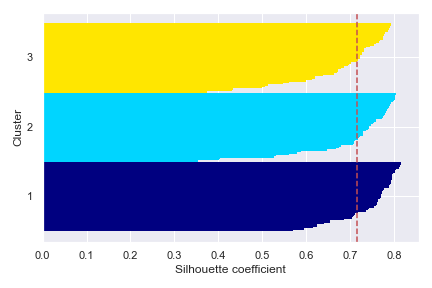
我們同時也可以比較 k=2,會發現其不符合上述指標。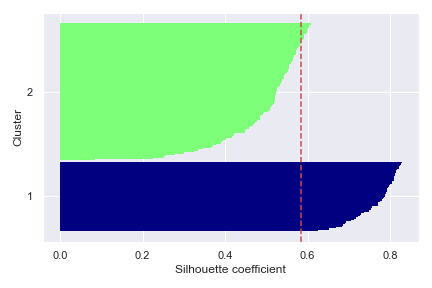
同為硬聚類的一種。將資料集逐次「合併或分裂」,直到要求的聚類數為止。
依照原理,層次聚類分成兩種方法:
將所有樣本視為一個聚類,將其逐步分割,直到達成指定聚類數為止。
反之,以每個樣本為聚類,不停將相近的聚類合併,直到達成指定聚類數為止。
凝聚層次聚類又根據對「聚類間距離」定義不同,分以下四種算法:
聚類間距定義:不同群聚中最近兩點間的距離。
特點:群聚的過程中產生「大者恆大」的效果,對離群很敏感。
聚類間距定義:不同群聚中最遠兩點間的距離。
特點:比較容易產生「齊頭並進」的效果,對離群很敏感。
聚類間距定義:不同聚類間點與點間的距離總和,取平均。
特點:比較容易產生「齊頭並進」的效果,較不受離群影響。
聚類間距定義:兩群合併後,聚類中各點到聚類重心的距離平方和。
覺得抽象的化,用 sklearn 內建的圖片來看就很易懂了:
我們用固定亂數 np.random.seed 產生作範例:
import pandas as pd
import numpy as np
np.random.seed(123)
variables = ['X', 'Y', 'Z']
labels = ['ID_0', 'ID_1', 'ID_2', 'ID_3', 'ID_4']
X = np.random.random_sample([5, 3])*10
df = pd.DataFrame(X, columns=variables, index=labels)
df
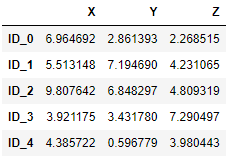
使用 pdist 計算點到點距離:
from scipy.spatial.distance import pdist, squareform
# pdist(X, metric=)
# X: nd-array,為 m*n 矩陣。
# metric: 距離求解法。默認 'euclidean'。
# 求解距離的函數。返回 Y 為 Cm取2 個觀察值之間的成對距離。
dis_vec = pdist(df, metric='euclidean')
dis_vec
>> array([4.973534 , 5.51665266, 5.89988504, 3.83539555, 4.34707339,
5.10431109, 6.69823298, 7.24426159, 8.31659367, 4.382864 ])
把每個點到點的間距用矩陣表示:
# squareform: 將向量形式的距離表示轉換成矩陣形式,或把矩陣形式轉為向量形式。
matrix = squareform(dis_vec)
row_dis = pd.DataFrame(
matrix,
columns=labels,
index=labels
)
row_dis
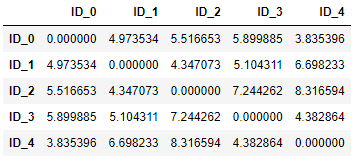
from scipy.cluster.hierarchy import linkage
row_clusters = linkage(df.values, method='complete', metric='euclidean')
pd.DataFrame(
row_clusters,
columns=['row label 1', 'row label 2', 'distance', 'no. of items in clust.'],
index=['cluster %d' % (i + 1) for i in range(row_clusters.shape[0])]
)
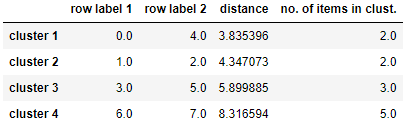
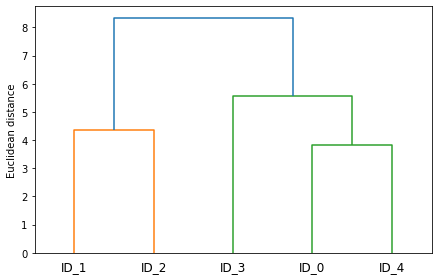
# 作圖
import matplotlib.pyplot as plt
from scipy.cluster.hierarchy import dendrogram
row_dendr = dendrogram(
row_clusters,
labels=labels,
)
plt.tight_layout()
plt.ylabel('Euclidean distance')
plt.show()
如果只想要得知分群結果,可用 sklearn 內建函數:
from sklearn.cluster import AgglomerativeClustering
ac = AgglomerativeClustering(
n_clusters=3,
affinity='euclidean',
linkage='complete'
)
labels = ac.fit_predict(X)
print(f'Cluster labels: {labels}')
>> Cluster labels: [1 0 0 2 1]
超參數:
1. n_clusters: 將要分成幾群。默認 2。
2. affinity: 用於計算鏈接的度量。默認 'euclidean'。
3. linkage: 使用哪個鏈接標準,'ward'(默認), 'complete', 'average', 'single'。
全名 Density-Based Spatial Clustering of Applications w/ Noise。
不同於 K-means 與 Hierarchical 藉距離定義聚類,DBSCAN 是以「密度」定義聚類。
開始前,我們需要定義兩個參數,分別是:
ε (eps):由這個參數值為半徑劃出的圓型區域稱為 ε-鄰域。
minPts:構成高密度區域需要最少有幾個點。
詳細步驟:
如下圖,即使單看點 C 會將其標籤為雜訊,但它同時也是點 A 聚類的一員。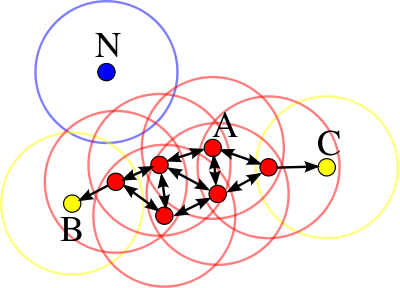
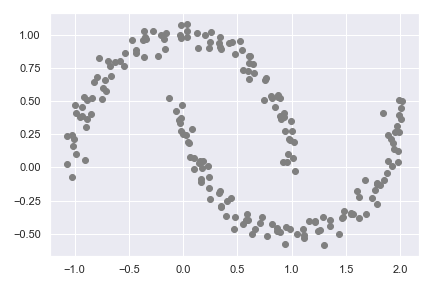
我們使用 make_moons 做範例:
from sklearn.datasets import make_moons
import matplotlib.pyplot as plt
X, y = make_moons(n_samples=200, noise=0.05, random_state=0)
plt.scatter(X[:, 0], X[:, 1], c='grey')
plt.tight_layout()
plt.show()
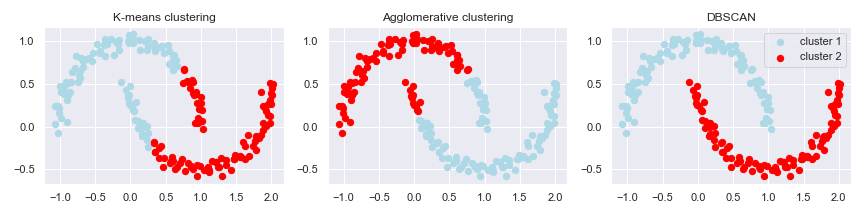
聚類方法:
# 用 K-means 做
from sklearn.cluster import KMeans, AgglomerativeClustering, DBSCAN
km = KMeans( n_clusters=2, random_state=0)
y_km = km.fit_predict(X)
# 用聚類分析做
ac = AgglomerativeClustering(n_clusters=2, affinity='euclidean', linkage='complete')
y_ac = ac.fit_predict(X)
# 用 DBSCAN 做
db = DBSCAN(eps=0.2, min_samples=5, metric='euclidean')
y_db = db.fit_predict(X)
超參數:
1. eps: 兩個樣本之間的最大距離,即 ε 。默認 0.5。
2. min_samples: 包括自身,將一個點視為核心點的鄰近樣本數(或總權重)。默認 5。
作圖:
f, (ax1, ax2, ax3) = plt.subplots(1, 3, figsize=(12, 3))
axis = [ax1, ax2, ax3]
y_ = [y_km, y_ac, y_db]
titles = ['K-means clustering', 'Agglomerative clustering', 'DBSCAN']
for a, y, t in zip(axis, y_, titles):
a.scatter(
X[y == 0, 0], X[y == 0, 1],
c='lightblue', marker='o', s=40, label='cluster 1'
)
a.scatter(
X[y == 1, 0], X[y == 1, 1],
c='red', marker='o', s=40, label='cluster 2'
)
a.set_title(t)
plt.legend()
plt.tight_layout()
plt.show()
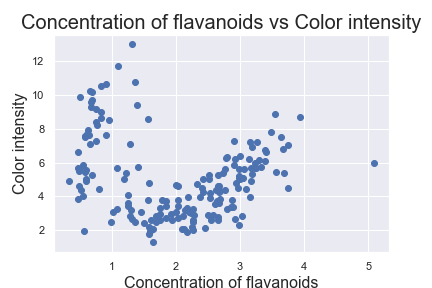
最後,DBSCAN 也可以用來找尋資料集中的離群,請看 wine 範例:
from sklearn.datasets import load_wine
ds = load_wine()
X = pd.DataFrame(ds.data, columns=ds.feature_names)[['flavanoids', 'color_intensity']]
y = pd.DataFrame(ds.target, columns=['Wine'])
# 作圖
plt.scatter(X.iloc[:, 0], X.iloc[:, 1], c='b', marker='o')
plt.xlabel('Concentration of flavanoids', fontsize=16)
plt.ylabel('Color intensity', fontsize=16)
plt.title('Concentration of flavanoids vs Color intensity', fontsize=20)
plt.show()
要注意的是這邊只把影響最大的因子 'flavanoids' 丟進 DBSCAN
X_data = X.iloc[:, 0:1].values
from sklearn.cluster import DBSCAN
db = DBSCAN(eps=0.2, min_samples=19).fit(X_data)
import numpy as np
y_pred = db.labels_
# 作圖
import matplotlib.pyplot as plt
plt.scatter(X.iloc[:, 0], X.iloc[:, 1], c=y_pred, marker='o')
plt.xlabel('Concentration of flavanoids', fontsize=16)
plt.ylabel('Color intensity', fontsize=16)
plt.show()
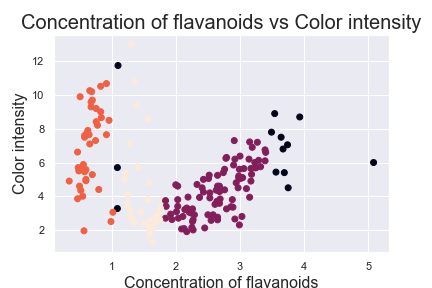
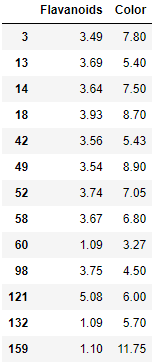
尋找 Outlier:
df[y_pred == -1]
若有需求,可到以下網站習得更多:
