上一篇我們的基因體時代-AI, Data和生物資訊 Day09-合成生物學與機器學習分享合成生物學領域跟機器學習的應用,跟Day08天的內容相似,也是一篇使用貝式集合模型來做實驗設計,減少測試數量,提高最終的目標輸出產量,不過在細節的算法這幾天會把他補上來,因為稍微複雜一點。
在COVID19後大家多多少少知道病毒是非常複雜的,且聽到病毒兩個字可能就會非常害怕,但其實病毒有非常多種,有的病毒可以用來發展基因治療,因其能把我們設計的基因放入到人體內,其中牽涉到複雜的機制,目前已經開始有些公司使用機器學習來設計及了解如何使用病毒載體來發展基因治療技術,如知名的Dyno,今天介紹其中一個熱門的病毒載體:腺病毒相關病毒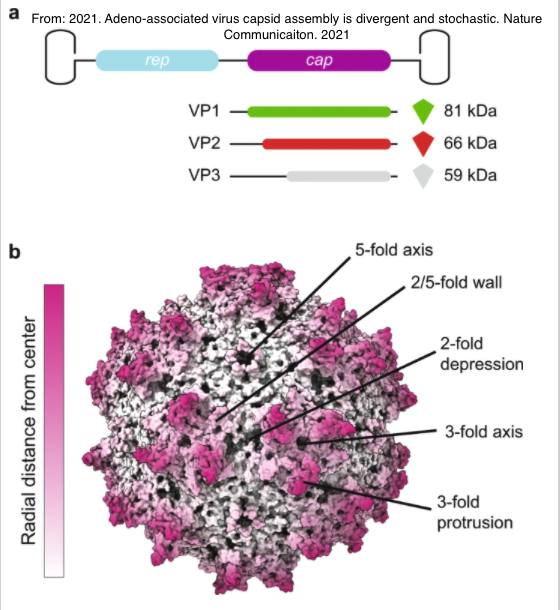
腺病毒相關病毒(Adeno-associated viruses)是小型、非致病、單股DNA之病毒,其屬於小病毒家族(Parvoviridae),其必須在腺病毒或皰疹病毒幫助下才能在宿主內複製,其內的基因大小為4.7kb,其中有三個重要的片段,分別是non-structural(rep), structural(cap), assembly activating(aap), membrane associated accessory(maap)。它的優勢在於低致病性以及多樣化的基因型態,其對不同組織有不同的喜好(tropism),重組過的腺病毒相關病毒可以包覆目標基因(Gene of Interest)。
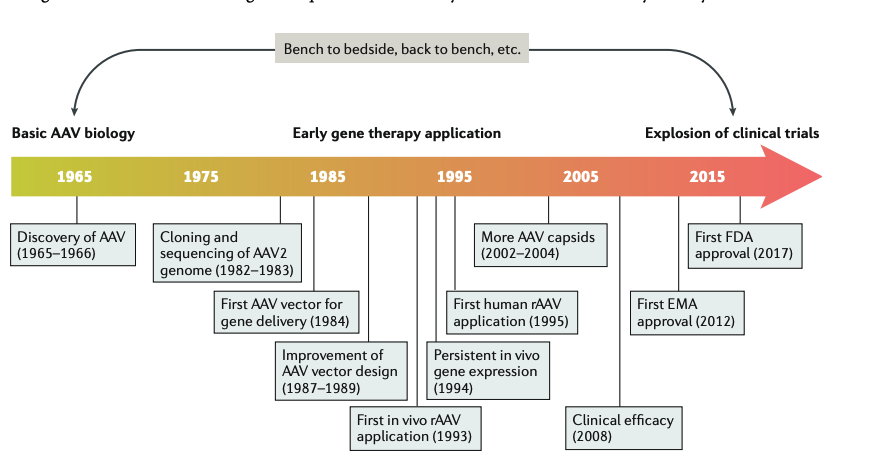
腺相關病毒作為治療的歷史其實也有快50年了,目前已有一些通過FDA的審核如Luxturna,EMA, Zolgensma, Glybera。
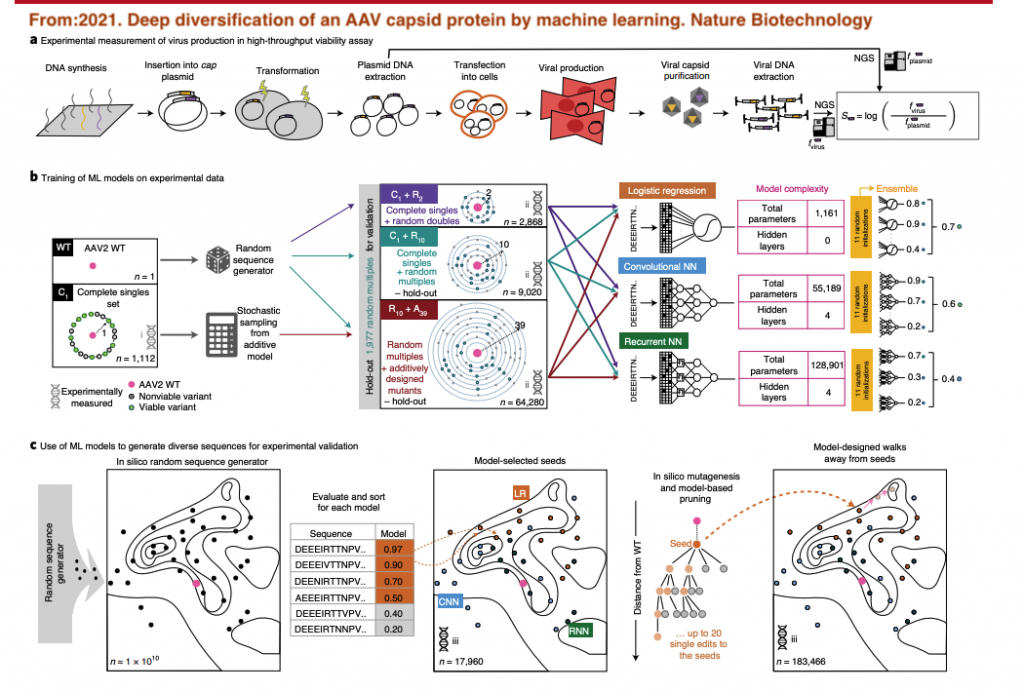
這邊的方式其實可以說是前兩天分享的方法的實戰篇,實際用來在設計擴增腺病毒相關病毒載體的可能性,此時就要根據場景來調整整個模型方式,以及所要設計的實驗內容,相對於前兩篇,我們要預測和設計的是實驗中各種化學物的濃度,和如何能提高產量,但在這邊我們要設計的是如何修改此病毒的基因序列來增加其生物多樣性(有點像是要增加不同的工具特性)。
為何需要這件事呢?因為腺病毒相關病毒是滿普遍存在在人類社會中的,所以很多人都有感染過,體內已有相關抗體,那這時候用此人抗體已經有中和能力的載體外鞘,那麼還沒有達到基因治療的效果前,就已經被人體內的免疫系統廓清了,所以藉由人工來擴增腺病毒相關病毒的外殼,大部分在cap片段的變異所產生的外殼,都無法正確組裝。
這篇研究(Deep diversification of an AAV capsid protein by machine learning. Nature Biotechnology. 2021)則是探索如何藉由修改cap片段的序列,來產生正常功能的外殼,已包覆載運到宿主細胞內之基因,事情實際上比想像中複雜,一個腺病毒相關病毒的外殼,共有60個capsid蛋白所組合,這個capsid蛋白主要有三種:VP1(713-738個氨基酸), VP2(580-610個氨基酸), VP3(524-544個氨基酸),都是由cap這個片段的基因所產生的。一個氨基酸由三個核酸序列所轉譯而成,藉由排列組合這些核酸序列來找尋可能且可以組裝病毒的外殼。
為了能產生給機器學習所用的資料,這篇研究一開始先使用一株天然存在的腺病毒相關病毒的核酸做起始,針對cap片段的DNA做修改,第一階段是一次只針對一個氨基酸上的核酸做置換,總共有1112個組合,其中約有58%是可以成功組合的外殼核酸設計,接者再往下隨機針對一次置換2-10個的氨基酸上之核酸做置換,1154個組合中只剩下0.3%是能再修改後正確組合成外殼核酸的設計。接者他利用這些資料來建立模型,進一步設計約56372個在cap片段有變異的病毒株都在2-39個變異之間,此時搭配機器學習的模型可以取得約62.5%的病毒株式是成功的,但值得注意的是其中1790株個別帶有大於21個變異的病毒組,全部都是不具有成功組合的結果。
明天看能否把他們的github細節來一探究竟!
這個月的規劃貼在這篇文章中我們的基因體時代-AI, Data和生物資訊 Overview,也會持續調整!我們的基因體時代是我經營的部落格,如有對於生物資訊、檢驗醫學、資料視覺化、R語言有興趣的話,可以來交流交流!
閱讀參考
Bryant, D.H., Bashir, A., Sinai, S. et al. Deep diversification of an AAV capsid protein by machine learning. Nat Biotechnol 39, 691–696 (2021). https://doi.org/10.1038/s41587-020-00793-4
Overcoming immunological challenges limiting capsid-mediated gene therapy with machine learning. Front. Immunol. 2021
Wörner, T.P., Bennett, A., Habka, S. et al. Adeno-associated virus capsid assembly is divergent and stochastic. Nat Commun 12, 1642 (2021). https://doi.org/10.1038/s41467-021-21935-5
Pierce J. Ogden, Eric D. Kelsic, Sam Sinai, George M. Church. Comprehensive AAV capsid fitness landscape reveals a viral gene and enables machine-guided design. Science, 2019; 366 (6469): 1139 DOI: 10.1126/science.aaw2900
Using a barcoded AAV capsid library to select for clinically relevant gene therapy. JCI Insight. 2019
Adeno-associated virus vector as a platform for gene therapy delivery, Nature Reviews Drug Discovery. 2019
Adachi K, Enoki T, Kawano Y, Veraz M, Nakai H. Drawing a high-resolution functional map of adeno-associated virus capsid by massively parallel sequencing. Nat Commun. 2014;5:3075. doi: 10.1038/ncomms4075. PMID: 24435020; PMCID: PMC3941020.
